生命科学基础研究的范式正在经历从“假设驱动”向“数据驱动”的重大转变。传统的假设驱动研究依赖于预设的已知信息,容易导致认知偏差,限制了对生物系统的全面理解。而数据驱动的研究方法则不预设影响变量,能够揭示更加全面的生物学现象。然而,海量数据对科学家的人力处理能力提出了极高的要求。
为了提高科研工作者对数据的处理能力,通过分析复杂数据,辅助研究者发现隐藏的生物学特征,从而将其转变为可以被认知的研究数据,为研究人员提供了全新维度的科研发现的可能性,加速了科学发现的进程。为此,我们举办了生命科学数据分析技能普及计划。
1.带领生命科学领域的科研工作者从零基础学会代码编程,能够个性化分析多组学数据2.系统学习多组学分析包括机器学习(临床预后模型)、转录组(RNAseq)、单细胞测序、表观遗传(Chipseq、ATACseq)、时空测序,一次学到位
3.将CNS文章数据分析内容全部学懂(理解)、学会(会敲代码分析)、学透彻(课题顶层设计和思路挖掘)、学以致用(用到标书申请和文章发表中)
4.掌握生命科学领域多组学分析,在大数据分析技术的加持下做出更有价值的科研成果!1.从19年开始到现在,我们在生信教育领域深耕五年之久,时间是最好的证明!
2.一对一指导、包教包会是我们开培训班五年来一贯的宗旨。我们敢承诺包教会的底气是来自多年的讲课经验和认真负责的态度。课程结束,答疑不结束!3.五年来华哥培训班的学员发表Cell、Nature、Science主刊文章7篇,子刊及一区文章累计超过90篇!部分学员成果展示如下: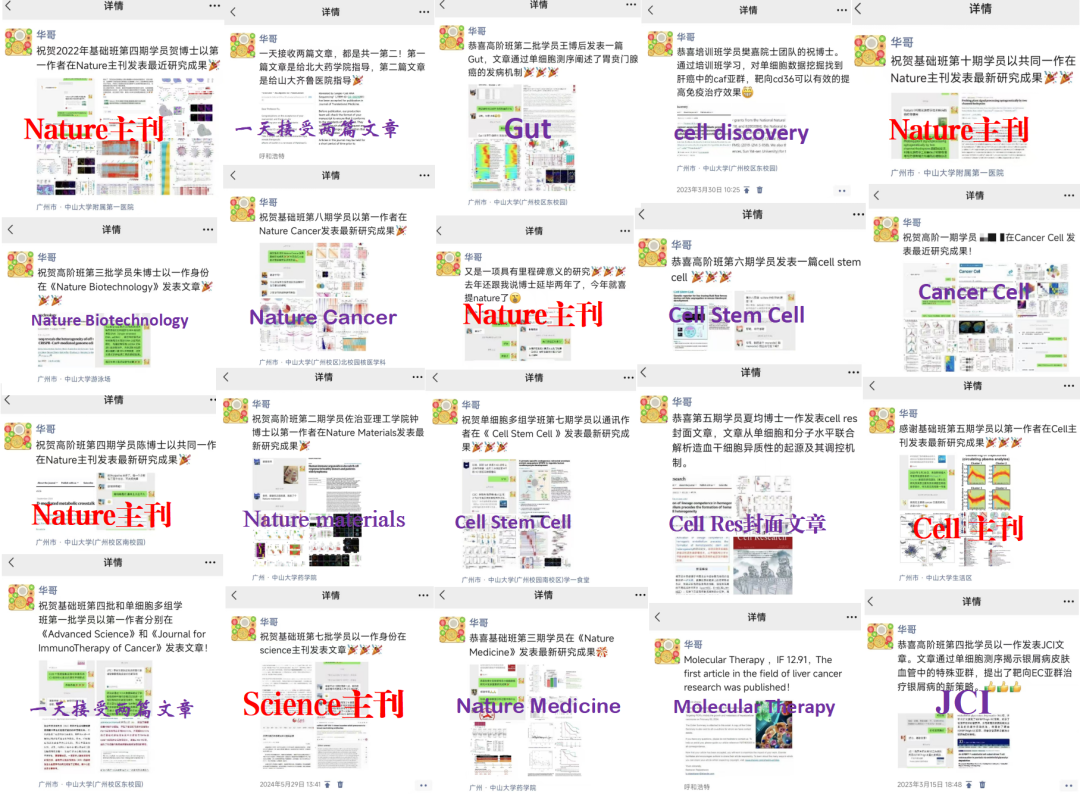
3.授课方式采用线上线下相结合,同步进行。线上腾讯会议直播课,互动答疑。线下在南京,现场教学更踏实!
4.深入剖析二十篇CNS文章的分析思路和分析方法,按照CNS文章源代码讲解,以文章的fig为例进行代码演示和复现学习,个性化分析第一节:编程基础学习--R语言
1.R和Rstudio的安装、环境配置
2.R语言简单语法及常见命令
3.以Cell文章方法描述学习R包的安装及使用
第二节:编程基础知识---数据结构
1.向量、矩阵、数据框和列表的创建和索引
2.多种数据结构的合并【Cell】
3.自定义Function函数构建
第三节:以Nature文章源代码学习转录组数据表达矩阵处理基本处理
1.重复基因和缺失值的删除
2.不同分组样本的批量归类【Nature】
3.多个样本的表达矩阵合并
第四节:以Cell文章源代码学习生存曲线
1.临床预后信息的批量整理
2.创建生存对象、拟合曲线【Cell】
3.特定基因的筛选构建预后分组
第五节:差异分析 RNAseq数据分析
1.芯片数据上游分析【Cancer Discovery】
2.多个样本的数据归一化处理
3.分组矩阵系统讲解【Nature】
4.Deseq2分析流程【Science】
第六节:以多篇CNS文章源代码学习画图
1.ggplot体系画图包括热图
2.火山图 箱线图 小提琴图【Nature】
3.多分组显著性p值添加方法【Nat Med】
4.三维pca图展示差异特征【Science】
第七节:基因集富集分析
1.over representation
2.GSEA 富集 【Cancer Cell】
3.包括自定义基因集的富集分析
4.富集通路网络图【Nat Genet】
第八节:以Nature文章为例系统讲解单细胞转录组基本分析
1.单细胞在CNS文章思路解析及常见图形解读
2.数据质控、数据放缩、PCA降维、聚类
3.三维tSNE、UMAP可视化【Science】
第九节 :单细胞转录组拟时序分析
1.monocle拟时序分析 【Nature】
2.细胞排序,构造一棵生成树
3.基因随轨迹分析变化热图【Cell】
4.BEAM轨迹分支分析【Nature】
5.自测和挖掘单细胞项目思路归纳总结
第十节:空间转录组理论及分析内容
1.空间转录组技术发展历程和原理介绍
2.空间转录组CNS文章思路解析及常见图解读
3.10x Visium 基本分析流程【Cancer Cell】
第十一节课:高分辨空间转录组分析
1.Xenium 空转数据分析【Nature】
2.Visium HD空转数据分析【Cell】
3.Stereo-seq “亚细胞级分辨率”测序介绍
4.空间测序多截面3D邻域重建【Nature】
第十二节课:机器学习基础理论
1.随机森林和支持向量机(SVM)
2.弹性网络回归算法Enet【Cell】
第十三节课:表观遗传研究
1.ChIP-seq、ATAC-seq在CNS文章中应用
2.ChIP-seq数据分析峰值可视化【Nature】
3.ATAC-seq数据peak注释【Cancer Cell】
第十四节:加权基因共表达网络分析 (WGCNA)算法系统讲解以nature文章为例
1.构建邻接矩阵和拓扑重叠矩阵
2.无尺度网络模型【Nature】
第十五节:免疫浸润计算
1.CIBERSORT反卷积算法,以TCGA数据为例
2.非监督共识聚类算法【Science】
3.转录因子富集【Cell Stem Cell】
第十六节:大数据分析在基金申请中应用
第十七节:实践课(课程总结,带领学员使用自测数据完成整体分析流程)
主讲老师华哥:中山大学博士,师从加州大学终身教授,一直钻研于单细胞多组学数据分析和机器学习算法研究,发表过多篇CNS子刊,参与过多项国自然重点、国家重大专项、孔雀计划等项目申报,在国内多家著名医院担任国自然标书指导老师,与多位院士团队和国外top实验室合作,指导过多篇CNS文章生信分析。
12月8日开始第一节课(一个月时间彻底掌握CNS文章基本数据分析)周六下午2:30--5:30、周日上午9:00--12:00、
周日晚上7:00--9:00
每周三节课,每节课三小时(时间全部在六日,不耽误工作日正常上班)线上:腾讯会议线上直播
为了保证技能普及计划质量和一对一指导服务,每一批只招五十人!每人:¥3880元(可开会务费 、培训费、数据分析费、测试费、测序技术服务费等发票
)
账 户 号:3602 0244 0920 1397 301同期举办:单细胞多组学班和空间转录组班,连报优惠待议(优惠价格联系招生老师)最详尽的CNS文章空间转录组数据分析教程
华哥生信团队正式成立!更多新课,更多优惠,更好的授课服务
